Darmmikrobiota und Antibiotika: Fehlendes Puzzlestück entdeckt
26.03.2024HIRI-Forschende haben eine kleine RNA nachgewiesen, die die Empfindlichkeit des Darmkeims Bacteroides thetaiotaomicron gegenüber bestimmten Antibiotika beeinflusst.
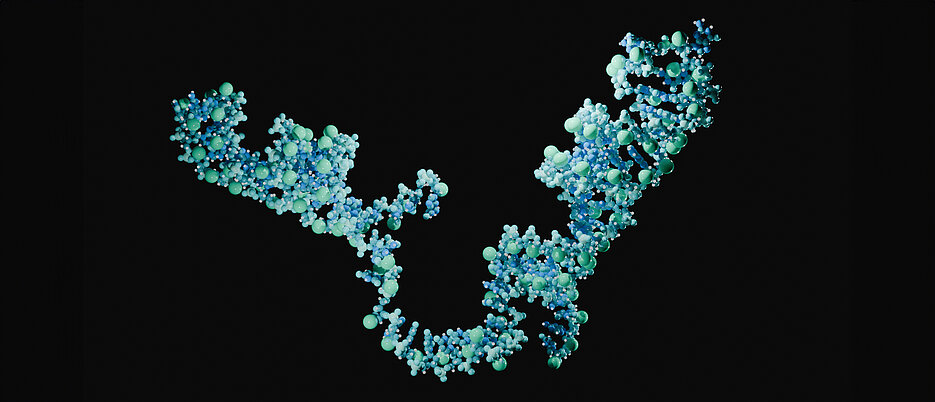
Wie sich Darmbakterien an ihre Umwelt anpassen, ist noch nicht vollständig entschlüsselt. Forschende des Würzburger Helmholtz-Instituts für RNA-basierte Infektionsforschung (HIRI) und der University of California, Berkeley, USA, konnten nun eine wichtige Lücke schließen: Sie haben eine kleine Ribonukleinsäure (sRNA) nachgewiesen, die die Anfälligkeit des Darmkeims Bacteroides thetaiotaomicron gegenüber bestimmten Antibiotika beeinflusst. Die Forschungsergebnisse, die heute in der Fachzeitschrift Nature Microbiology veröffentlicht wurden, könnten die Grundlage für neue Therapien bei Darmerkrankungen und für die Bekämpfung von Antibiotikaresistenzen bilden.
Der Darm spielt eine entscheidende Rolle für das Wohlbefinden des Menschen. Als komplexes Ökosystem unzähliger Mikroorganismen kann die Darmmikrobiota durch Faktoren wie Ernährungsumstellung, Medikamenteneinnahme oder Gallensalze beeinflusst werden – mit Auswirkungen auf die Gesundheit. Zu den dominierenden Bakterienarten im menschlichen Darm gehören Bacteroides thetaiotaomicron. Diese Mikroben spalten Mehrfachzucker bei der Verdauung und sind für die Gesundheit des Menschen nützlich. Gleichzeitig können sie aber auch Infektionen begünstigen, wenn das intestinale Gleichgewicht gestört ist, zum Beispiel nach einer Antibiotikabehandlung. Die molekularen Mechanismen, die es diesen Darmkeimen ermöglichen, sich an ihre Umgebung bestmöglich anzupassen, sind jedoch weitgehend unbekannt.
„Meine Gruppe und ich wollen verstehen, wie sich Bacteroides thetaiotaomicron an veränderte Bedingungen im Darm anpassen“, fasst Alexander Westermann das Ziel der Studie zusammen, die heute in der Fachzeitschrift Nature Microbiology erschienen ist. Der Initiator der wissenschaftlichen Arbeit ist Forschungsgruppenleiter am Würzburger Helmholtz-Institut für RNA-basierte Infektionsforschung (HIRI), einem Standort des Braunschweiger Helmholtz-Zentrums für Infektionsforschung (HZI) in Kooperation mit der Julius-Maximilians-Universität Würzburg (JMU).
Um die Netzwerke der Transkription – der Umschreibung von DNA in RNA – in Bacteroides thetaiotaomicron zu beleuchten, haben das HIRI-Team in Zusammenarbeit mit Forschenden der University of California, Berkeley, in den USA Transkriptionseinheiten kartiert und Profile ihrer Expressionsniveaus unter verschiedenen experimentellen Bedingungen erstellt.
Der Vergleich dieser Expressionswerte mit Literaturdaten zur Fitness von genetisch veränderten Bakterienvarianten ermöglichte dem Forschungsteam einen ganzheitlichen Blick auf die regulatorischen Netzwerke und die funktionelle Rolle von sRNAs bei der bakteriellen Anpassung. „Unsere Erkenntnisse bieten neue Einblicke in das komplexe Zusammenspiel zwischen Umweltfaktoren, Genexpression und bakterieller Fitness“, betont Westermann, der zudem eine Professur an der JMU innehat.
Kleine RNA steuert Antibiotikaempfindlichkeit
Bei der Untersuchung des Nukleinsäuregehalts von Bacteroides thetaiotaomicron konnte das Team ein spezifisches regulatorisches RNA-Molekül – eine kleine RNA (sRNA, von engl. small ribonucleic acid) – nachweisen, das die Empfindlichkeit des Bakteriums gegenüber Tetracyclin-Antibiotika beeinflusst. „Mit der Entdeckung der sRNA MasB und ihrer Rolle bei der Steuerung der Antibiotikaempfindlichkeit haben wir Licht auf einen bisher nicht charakterisierten Regulationsmechanismus geworfen“, ordnet Erstautor und Postdoktorand Daniel Ryan das Ergebnis ein. Die Befunde geben Aufschluss über den Einfluss von Antibiotikabehandlungen auf die Mitglieder der Mikrobiota. Auf dieser Grundlage könnten neue Strategien zur Vermeidung von antibiotikabedingten Kollateralschäden an nützlichen Bakterien entwickelt und Therapeutika verbessert werden.
Die Forschung stellt eine wertvolle Informationsquelle für die Mikrobiom-Gemeinschaft dar: Der umfassende Transkriptom-Atlas, der über den Webbrowser „Theta-Base“ öffentlich zugänglich ist, bietet die Möglichkeit, weitere sRNAs zu untersuchen und ihre Funktionen in diesem Zusammenhang zu erforschen. „Die RNA-Biologie von Bacteroides und anderen Mitgliedern der Darmmikrobiota ist vergleichsweise wenig erforscht. Projekte wie dieses legen den Grundstein für zukünftige Studien und stellen eine wichtige Ressource für weitere Forschungsarbeiten dar“, sagt Westermann.
Förderung
Die Studie wurde durch die Deutsche Forschungsgemeinschaft (DFG), den Europäischen Forschungsrat (ERC Starting Grant) und die US National Institutes of Health gefördert.
Originalpublikation
Ryan D, Bornet E, Prezza G, Alampalli SV, de Carvalho TF, Felchle H, Ebbecke T, Hayward R, Deutschbauer AM, Barquist L, Westermann AJ. An expanded transcriptome atlas for Bacteroides thetaiotaomicron reveals a small RNA that modulates tetracycline sensitivity. Nature Microbiology (2024), DOI: 10.1038/s41564-024-01642-9
Helmholtz-Institut für RNA-basierte Infektionsforschung
Das Helmholtz-Institut für RNA-basierte Infektionsforschung (HIRI) ist die weltweit erste Einrichtung ihrer Art, die die Forschung an Ribonukleinsäuren (RNA) mit der Infektionsbiologie vereint. Auf Basis neuer Erkenntnisse aus seinem starken Grundlagenforschungsprogramm will das Institut innovative therapeutische Ansätze entwickeln, um menschliche Infektionen besser diagnostizieren und behandeln zu können.
Das HIRI ist ein Standort des Braunschweiger Helmholtz-Zentrums für Infektionsforschung (HZI) in Kooperation mit der Julius-Maximilians-Universität Würzburg (JMU) und befindet sich auf dem Würzburger Medizin-Campus.